Initialising ...
Initialising ...
Initialising ...
Initialising ...
Initialising ...
Initialising ...
Initialising ...
Schyman, P.*; Danielsson, J.*; Pinak, M.; Laaksonen, A.*
Journal of Physical Chemistry A, 109(8), p.1713 - 1719, 2005/02
被引用回数:39 パーセンタイル:77.29(Chemistry, Physical)DNA損傷の修復酵素であるヒト8-オキソグアニンDNAグリコシラーゼがグリコシル結合を切断する際の活性リジン(Lys 249)の働きについて調べた。このリジンは、プロトンをアスパラギン酸塩へ供給することにより活性化した後に、S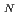 2タイプの反応により求核試薬として働くと考えられてきた。本研究では、会合と解離プロセスを調べるのに、ハイブリッド密度汎関数理論を用いた。その結果、反応最小エネルギーバリアがS
2タイプの反応により求核試薬として働くと考えられてきた。本研究では、会合と解離プロセスを調べるのに、ハイブリッド密度汎関数理論を用いた。その結果、反応最小エネルギーバリアがS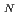 1タイプのメカニズムを含むことを見いだした。S
1タイプのメカニズムを含むことを見いだした。S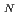 1タイプのメカニズムでは、リジンが静電的に解離基を安定化し、非常に小さなバリアでプロトンを供給し、最終的にペントース環を攻撃して共有結合で結ばれたタンパク質とDNA中間複合体をつくる。これは、このタイプの酵素の反応にとって、解離メカニズムが頻繁に起こりうるモードであるという仮説をサポートしている。
1タイプのメカニズムでは、リジンが静電的に解離基を安定化し、非常に小さなバリアでプロトンを供給し、最終的にペントース環を攻撃して共有結合で結ばれたタンパク質とDNA中間複合体をつくる。これは、このタイプの酵素の反応にとって、解離メカニズムが頻繁に起こりうるモードであるという仮説をサポートしている。
Pinak, M.
JAERI-Research 2002-016, 31 Pages, 2002/09
突然変異を誘発するDNA酸化損傷 である8-oxoGについて、損傷DNAの単独存在下、及びヒト修復酵素オキソグアニングリコシレース1 (hOGG1)との共存下で分子動力学的シミュレーションを行い、DNA分子の構造変化とDNA-酵素複合体の形成に関わる動力学的過程の検討を行った。シミュレーションには、中心位に8-oxoG分子を挿入したB型DNAヌクレオチド鎖を用いた。DNAのみのシミュレーションでは、水素結合の切断によって部分的に構造が破壊されたB型DNAが観察され、8-oxoG挿入位から1塩基対分離れた相補鎖側のアデニンがDNA二重鎖からフリップアウトしていた。DNAと修復酵素hOGG1共存下のシミュレーションでは、分子動力学的シミュレーション開始後500psでDNA-酵素複合体が形成され、シミュレーションが終了する1ns後まで安定していた。アルギニン313のN末端は、8-oxoGを持つヌクレオチドのリン酸ジエステル結合に近接し、酵素のアミノ酸とDNA損傷との化学反応を可能にしている。8-oxoGの5'位のリン酸ジエステル結合は、アルギニン313のN末端に近接した位置に移動していた。さらに、DNAと酵素の近接箇所では水分子を介した水素結合が形成され、複合体の安定性を高めていた。